介绍 基孔肯雅病毒(CHIKV)是一种蚊子传播的甲型病毒,属于多哥病毒科[ 1 , 2 ]. 1952年坦桑尼亚疫情首次将其隔离[ 三 ]. 它是突发性急性感染的原因,其特征是高烧、关节痛、肌痛、头痛和皮疹[ 4 , 5 ]. 多关节痛是该病的典型临床症状,非常疼痛。 症状通常为自限性,持续1至10天。然而,关节痛可能持续数月或数年。 在一些患者中,也有轻微出血症状,如鼻出血或牙龈吞咽。
CHIKV在地理上分布于非洲、印度和东南亚。 在非洲,病毒是通过野生灵长类动物和蚊子之间的森林传播循环维持的,例如 黄斑伊蚊, 或 A.泰勒 [ 4 ]. 在亚洲,CHIKV主要通过以下途径在人与人之间传播 埃及伊蚊 在较小程度上 白纹伊蚊 通过城市传输循环。 自1952年坦桑尼亚疫情以来,CHIKV已在东非(坦桑尼亚和乌干达)、南部非洲(津巴布韦和南非)、西非(塞内加尔和尼日利亚)和中非(中非共和国和刚果民主共和国)引发疫情[ 4 ]. 最近一次疫情再次爆发是在1999-2000年金沙萨,那里估计有50000人受到感染[ 6 ]. 自从1958年在泰国曼谷首次有记录的亚洲疫情爆发以来,泰国、柬埔寨、越南、老挝、缅甸、马来西亚、菲律宾和印度尼西亚都有疫情爆发的记录[ 4 , 5 ]. 最近一次疫情再次爆发是在20年后的2001-2003年,在爪哇[ 7 ]. 在非洲和亚洲,疫情的再次爆发是不可预测的,连续疫情之间的间隔时间为7至8年至20年。
自2004年底以来,印度洋西南部岛屿出现了CHIV。 2005年1月至3月期间,科摩罗报告了5000多起病例。 2005年晚些时候,该病毒在其他岛屿传播,即马约特岛、塞舌尔岛、留尼汪岛和毛里求斯。 从2005年12月开始,雨季导致病毒重新流行。 自2006年1月1日以来,马约特岛、毛里求斯和塞舌尔群岛各报告了数千例病例( 网址:http://www.invs.sante.fr 2006年4月21日)。 受影响最严重的岛屿是留尼汪岛(总人口:770000),估计有244000例(2006年4月16日)。 最近,马达加斯加和印度也有病毒传播的记录。
在留尼汪岛,第一批记录在案的病例是2005年3月从科摩罗返回的患者。 3月至6月报告的病例超过3000例[ 8 ]. 在南半球的冬季,传播受到限制(每周50-100例),从12月中旬开始出现了一次大的传播高峰[ 8 ]2005年估计有12400例,2006年(2006年4月16日)估计有231600例。 2006年的发病高峰出现在2月的第二周,超过45000例。 病例数量现已减少,4月第二周估计有3000例。自2005年3月以来,123名确诊为CHIKV感染的患者出现了严重的临床症状(神经症状或重型肝炎),有理由在重症监护病房住院。 一些脑病和严重疼痛综合征病例与病毒的垂直传播有关( 网址:http://www.invs.sante.fr ).
CHIKV是一种包膜阳性RNA病毒。 迄今为止,已确定Ross和S27菌株的两个CHIKV完整核苷酸序列[ 9 ]都是在1952年坦桑尼亚疫情期间从患者身上分离出来的。 另一个完整的核苷酸序列已确定为一株在 A.分叉 1983年塞内加尔疫情期间 AY726732号 ). Khan等人[ 9 ]结果表明,S27基因组的结构与其他α病毒相似,O'nyong-nyong病毒(ONN)是与CHIKV关系最近的病毒。 此外,基于非洲和亚洲分离物的部分E1序列进行的系统发育分析显示存在三个不同的CHIKV谱系群:一个包含所有西非分离物,一个包含亚洲分离物,以及一个对应于东非、中非和南部非洲分离物[ 10 ]. 1999-2000年在刚果民主共和国分离出的菌株属于后一类[ 6 ].
在本研究中,我们测定了从来自留尼汪岛和塞舌尔群岛的六名患者分离的病毒的几乎完整的核苷酸序列。 此外,从留尼汪岛、塞舌尔、马达加斯加、马约特岛和毛里求斯共127名患者的血清或脑脊液(CSF)中检测到部分E1序列。 我们的目标是确定印度洋疫情分离株的基因组结构和独特的分子特征,这可能会将它们与其他报道的CHIKV和α病毒序列区分开来。 此外,还对印度洋爆发的CHIKV菌株的系统发育起源、多样性和微进化进行了研究。
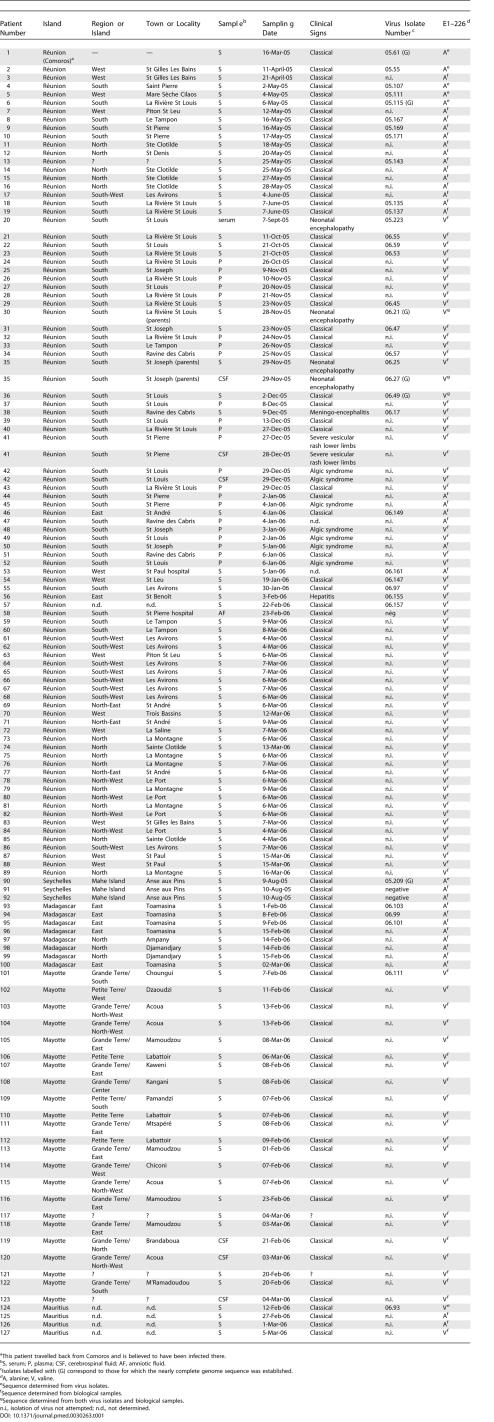
方法 患者 127例被检测出部分或完整CHIKV核苷酸序列的患者来自Réunion( n个= 89),塞舌尔( n个= 3) ,马达加斯加( n个= 8) ,马约特( n个= 23)和毛里求斯( n个= 4). 患者特征和生物样本列于 表1 .
表1。
特异性小鼠免疫血清和间接免疫荧光检测 巴斯德研究所制备了针对CHIKV的小鼠超免疫腹水(HMAF)。 先前描述了针对法国嗜神经病毒黄热病病毒株、登革热1型病毒哈瓦伊株或西尼罗河病毒IS-98-ST1株的HMAF[ 11 ]. 简言之,通过用来自新生小鼠的感染病毒的大脑的粗提取物重复免疫成年小鼠,然后接种肉瘤180,获得特异性HMAF。 首次免疫后1个月收集小鼠抗血清。 所有动物实验均按照巴斯德研究所动物护理办公室实验室的指南进行。
对于间接免疫荧光分析,将蚊子细胞用甲醇/丙酮(7 Vol/3 Vol)在−20°C的玻璃斑点上固定20分钟。简言之,将固定的细胞与特定的HMAF在室温下在PBS中以1:200的稀释度孵育20分钟。用PBS大量洗涤后, 细胞进一步与FITC-结合的山羊抗鼠IgG抗体(Pierce Biotechnology,Rockford,Illinois,United States)在PBS中以1:100的稀释度孵育。用荧光显微镜检查载玻片。
CHIKV分离和病毒RNA提取 从人血清或脑脊液中分离出CHIKVs( 表1 ). 白纹伊蚊 将1 ml血清或1:10稀释的脑脊液接种在Leibovitz-L15培养基(Invitrogen/Gibco,Carlsbad,California,United States)中的C6/36细胞。 细胞在28°C的Leibovitz-L15培养基中生长,补充5%热灭活胎牛血清(FBS)和10%胰蛋白酶磷酸盐。 在第一代(5 d)和第二代(7 d)后收集细胞和上清液。 用抗CHIKV HMAF间接免疫荧光法鉴定病毒株为CHIKV。 对于基因组已测序的临床分离株05.115、06.21、06.27和06.49,使用特定HMAF进行免疫荧光分析,确认没有黄热病病毒、登革热1型病毒和西尼罗河病毒。
根据制造商建议的程序,使用NucleoSpin RNA II试剂盒(德国杜伦市Machery-Nagel)或QIAAmp viral Minikit试剂盒(法国科塔布夫-塞德克斯市Qiagen)从CHIKV分离物中提取病毒RNA。 分离物05.115、06.21、06.27和06.49的非结构区序列是从第二代传代后采集的上清液中提取的RNA中测定的。 所有其他CHIKV分离株序列都是使用从第一代中提取的模板RNA获得的。 使用QIAAmp viral Minikit从生物样本中提取病毒RNA。
焦点免疫分析
假黄芩 AP61细胞在含有10%FBS的Leibovitz L-15生长培养基中的24孔组织培养板中生长24 h。用Leibovitiz L-15清洗蚊子细胞单层,并添加0.2 ml Leiboviz L-15/2%FBS。 细胞在0.2 ml Leibovitz L-15/2%FBS中感染CHIKV,并在28°C下培养1 h。然后添加0.4 ml Leibowitz L-15%FBS和羧甲基纤维素(1.6%)组成的覆盖培养基,并将组织培养板在28°C下培养2 d。 如前所述,通过焦点免疫分析显示感染细胞的病灶[ 11 ]. 用PBS清洗细胞,用3%多聚甲醛在PBS中固定20分钟,并在室温下用0.5%Triton X-100在PBS内渗透4分钟。 将固定细胞在37°C下与1:2000稀释的HMAF(针对CHIKV)孵育20分钟。 将辣根过氧化物酶结合的山羊抗鼠IgG抗体用作第二抗体(1:100稀释),在37°C下持续20分钟。用DAB过氧化物酶底物(美国密苏里州圣路易斯Sigma)观察Foci。 使用自动测量功能,使用AxioVision 4.5版程序(德国奥伯克郡卡尔蔡司)计算焦距。
核苷酸测序 底漆( 表S1 )根据S27菌株的核苷酸序列设计。 使用Titan One Tube RT-PCR试剂盒(法国梅兰罗氏)进行RT-PCR。 测序前通过超滤纯化RT-PCR片段(法国莫尔斯海姆Millipore)。 使用BigDye Terminator v1.1循环测序试剂盒(美国加利福尼亚州福斯特市应用生物系统公司)进行测序反应,并通过乙醇沉淀进行纯化。 序列色谱图是在自动序列分析仪ABI3100或ABI3700(应用生物系统)上获得的。 所有扩增子在两条链上测序。
基因组序列的组装和序列分析 Contig组装由不同的操作员和软件独立执行,使用BioNumerics 4.5版(比利时Sint-Martens-Latem的Applied-Maths)或PhredPhrap/Conced[ 12 ]. 两种分析得出的所有菌株的一致序列完全相同。 对这六个菌株获得了一个单一的对照。 使用程序BioNumerics(DNASP 4.10版)进行序列比对和代换表计算[ 13 ]和DAMBE版本4.2.13[ 14 ]. 使用ClustalW 1.7版对核苷酸和氨基酸(aa)序列与选定的α病毒序列进行比对[ 15 ]. 使用PHYLIP包计算序列恒等式[ 16 ]. 使用维也纳RNA二级结构服务器预测RNA二级结构[ 17 ]. 使用MEGA 3.1版构建邻接树[ 18 ]具有多次替换的Kimura-2参数校正。 节点的可靠性通过bootstrap重采样1000次来评估。 使用DNASP估计每个同义位点的同义替换量(Ks)和每个非同义位点(Ka)的非同义替换。 RDP2号机组[ 19 ]用于检测假定的镶嵌序列。
三维结构建模 中性pH下Semliki森林病毒(SFV)糖蛋白E1外结构域的晶体结构[ 20 ]作为模板,对印度洋分离物的两个aa突变进行建模和分析。 使用RIBBONS程序绘制3D结构图[ 21 ].
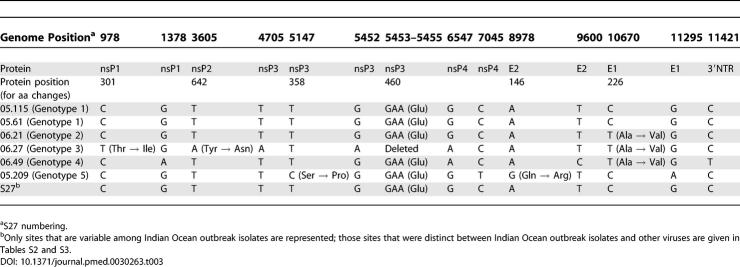
结果 印度洋CHIKVs暴发的基因组结构和分子特征 基因组组织。 我们测定了代表不同地理起源、时间点和临床形式的六株CHIKV分离株(05.115、05.61、05.209、06.21、06.27和06.49)的接近完整的基因组序列( 表1 )印度洋疫情的爆发。 测定了11601个核苷酸,对应于1952年坦桑尼亚分离物S27(全长11826 nt)核苷酸序列中的52位(5′非翻译区[NTR])至11667位(3′NTR,第三重复序列末端)。 S27和Réunion分离株之间有三个插入/缺失事件,其中两个在3′NTR中观察到。 首先,S27(11440–11443)中观察到的14个核苷酸的内部poly-A延伸,与可能的内部poly-A位点相对应[ 9 ]在印度洋分离物中被仅5 a的延伸所取代,类似于在其他CHIKV中观察到的情况,例如罗斯菌株。 其次,S27位置11625处5-A延伸的印度洋分离物中缺少一个A。 最后,分离物06.27中缺少一个密码子,对应于nsP3密码子460,在该密码子处分析了所有其他印度洋分离物,可用的α病毒序列为GAA,编码Glu。
本文中提出的六个分离株的基因组序列与先前报道的甲病毒的基因组序列相似[ 9 , 22 , 23 ]. 编码序列由两个大的开放阅读框组成,分别为7422nt和3744nt,编码非结构多蛋白(2474aa)和结构多蛋白(1248aa)。 非结构多蛋白是蛋白质nsP1(535 aa)、nsP2(798 aa),nsP3(530 aa)和nsP4(611 aa)的前体,而结构多蛋白则是蛋白质C(261 aa,E3(64 aa,E2(423 aa,6K(61 aa)以及E1(439 aa)。 α病毒家族的裂解位点和E3、E2和E1中的糖基化位点是保守的。 在非结构开放阅读框的终止密码子(TAG,7499–7501)和结构开放阅读框架的起始密码子(7567–7569)之间鉴定出一个65-nt连接序列。 5英尺NTR在76号位置结束。 3′NTR区起始于11314位,包含三个具有预测二级结构的重复序列元件( 图S1 )与之前的工作一致[ 9 ].
印度洋暴发菌株和S27菌株之间的差异。 与S27菌株相比,Réunion分离物05.115(与S27关系最密切;见下文)在非结构蛋白中表现出28个aa的变化(1.13%)( 表S2 )其中nsP3的比例最高(2.26%),nsP2的比例最低(0.6%)。 nsP3中12个aa变化中有10个集中在326和524位之间(5.0%变异),与ONN病毒中的结果类似[ 24 ]. 与S27的一个重要区别是,印度洋分离株在nsP3密码子524处显示出蛋白石终止密码子(UGA),而不是S27中的Arg(CGA)。 这种蛋白石密码子在相关的α病毒中被观察到[ 9 , 23 , 24 ],并被认为通过一种通读机制调节nsP4的表达,nsP4是一种假定的RNA聚合酶[ 22 , 25 ].
与S27相比,分离物05.115的结构蛋白显示21个(1.68%)aa替换( 表S3 ). 值得注意的是,包膜蛋白E2的变异最大,其中14个(3.3%)aa变化,高于包膜蛋白E1(0.68%)和衣壳蛋白(0.38%)。 S27和05.115分离株之间同义和非同义位点的进化率之比(Ks/Ka)对于整个多蛋白为11.0,而对于E2蛋白仅为6.12,这可能表明有利于该免疫原性蛋白中aa变化的阳性选择。 相比之下,非结构多蛋白的Ks/Ka为18.75。
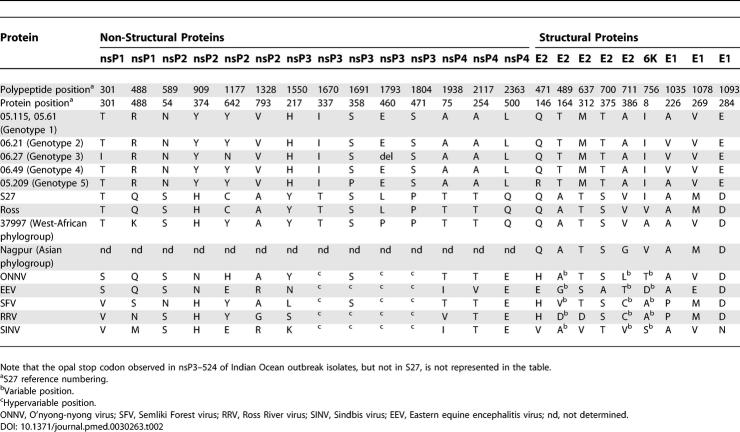
印度洋爆发的非结构蛋白分子特征和表型变异。 与其他CHIKV序列相比,10个位点(不包括多态性位点)具有爆发菌株非结构蛋白特有的aa( 表2 ). 在相对保守的位置观察到四种变化:nsP2-54、nsP2-374、nsP4-254和nsP4-500。 有趣的是,后一个位置约为催化“GDD”基序的30 aa,是印度洋序列中的Leu,而不是其他CHIKV序列中的Gln,以及所有其他α病毒中严格保守的Glu。 其余六项变化发生在相对可变的地区( 表2 ).
表2。 印度洋分离物与阿尔法病毒序列选择之间的相关氨基酸变化
在菌株05.209(nsP3-S358P)和06.27(nsP1-T301I、nsP2-Y642N和nsP3-460del)中观察到其他特异性变化。 值得注意的是,表型分析显示菌株06.27存在差异。 焦点免疫分析显示,低侵袭CHIKV 05.115、06.21、06.27和06.49在 白纹伊蚊 C6/36(未发布数据)和 假鳞甲 AP61细胞( 图S2 A) 形成微小、小型和中型病灶的混合物。 计算分析表明,与其他菌株相比,CHIKV 06.27在AP61细胞单层上表现出更大的病灶( 图S2 B) ●●●●。 CHIKV 06.27的特殊表型可能归因于参与病毒复制的nsP中的aa差异[ 22 ]. 目前正在进行研究,以确定nsP1-T301I、nsP2-Y642N和nsP3-460del的变化是否会改变蚊子细胞中CHIKV 06.27的生长。
结构蛋白和3D建模中的印度洋分子特征。 在分析结构蛋白的aa序列时,发现7个位置(4个在E2中,1个在6K中,2个在E1中)是印度洋疫情分离株所特有的( 表2 ). 其中两个位于E2外结构域,在我们的分离物中鉴定出Thr 164和Met 312,而在所有其他可用的CHIKV序列中分别鉴定出Ala和Thr( 表2 ). 这两个位置中的第一个在字母病毒中是可变的; 它位于先前定义为含有中和表位的区域[ 5 , 26 ]. 在312位,Thr存在于其他CHIKV、ONNV和SFV中,但在其他α病毒中有所不同。 该位置位于E1-E2齐聚的重要区域[ 5 , 26 ].
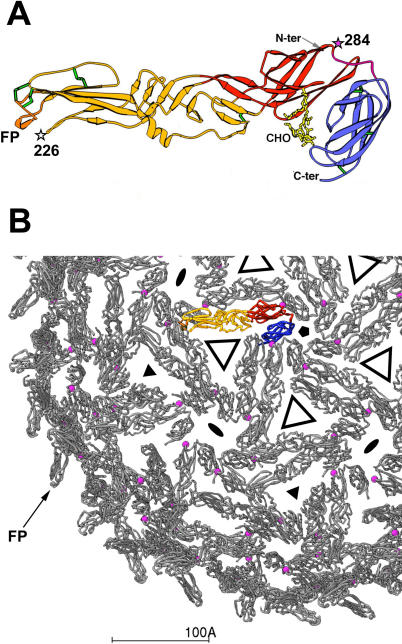
在E1中,观察到两个关键的替换:一个位于284号残基,专一于印度洋菌株,另一个位于226号残基上,存在于六分之三的印度洋菌株中(06.21、06.27和06.49)。 这两个突变都被映射到3D结构上(根据SFV E1的晶体结构建模) 图1 有趣的是,在所有先前报道的CHIKV序列中,残基226为Ala( 表2 )在疫情爆发之初(2005年3月和5月)获得的印度洋分离物中也含有丙氨酸。 2005年11月和12月从患者身上获得的后续分离物在该位置显示Val(见下文)。 虽然226位在α病毒中相对可变,但观察到该位(Pro-to-Ser)的单一突变使SFV能够适应缺乏胆固醇的昆虫细胞的生长[ 27 , 28 ].
图1。 根据SFV E1晶体结构建模的3D结构上E1变化的定位。
(A) E1的带状图,域I为红色,域II为黄色,域III为蓝色。 绿色的管子标记着二硫键。 在分子末端(在结构域II中)的融合肽被染成橙色并被标记。 晶体中观察到的N端和C端(跨膜区上游30 aa处)也被标记。 在印度洋分离物中观察到的两个独特变化由恒星表示并标记为:位置226(白色)和284(洋红色)。
(B) 从5倍对称轴向下观察,二十面体E1支架在病毒粒子表面的部分表示(一个八分体,略微延伸)。 一个E1原聚体以颜色突出显示,如(A)所示; 所有其他的都用灰色表示。 一些二十面体对称轴的位置绘制为实心黑色符号:五边形表示5倍轴,三角形表示3倍轴,椭圆表示2倍轴(字母病毒T=4晶格中的椭圆与准6倍轴重合)。 开放三角形大致表示与E1紧密相互作用的E2三聚体的位置,涵盖结构域II和融合肽,并呈现主要抗原位点。 开放三角形也标志着T=4表面二十面体晶格的准三重对称轴。 一个洋红色的球标记着Glu 284的位置,位于E1间原聚体接触点。 这种接触在表面晶格上传播了240次(注意,所有粉红色的球都画在灰色的原生质体上)。 请注意,橙色的融合肽指向上方并远离与其他E1原生质体的接触。 这更容易在病毒粒子的外围看到,其中一个被标记为(FP)。 在病毒粒子中,E1的这个区域是不可接近的,覆盖在E2分子下面[ 20 ].
在印度洋分离物E1中观察到的另一种独特氨基酸是Glu 284。 这是一个高度保守的位置,在大多数α病毒中显示Asp,在SINV中显示Asn( 表2 ). 该aa位于病毒粒子表面E1原体之间的界面,参与构成二十面体E1支架的接触( 图1 ).
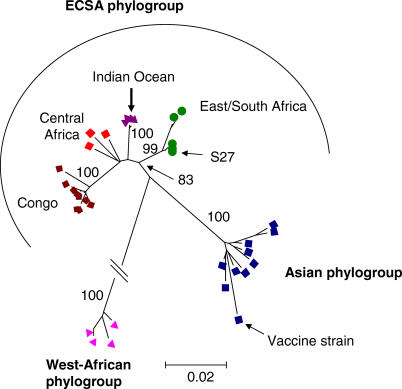
系统发育分析 先前基于E1蛋白序列的研究表明CHIKV物种具有很强的系统地理结构[ 6 , 10 ]. 为了确定印度洋暴发菌株的祖先谱系群,我们将来自六个完整基因组的E1编码序列(位置271-1314,即密码子91-438)中的1044-nt区域与29个其他可用的基孔肯亚序列进行了比较( 表S4 ). 系统发育分析( 图2 )清楚地表明,目前的印度洋分离物代表了一个由来自东非、中非和南非的分离物组成的广泛群中的同质分支(ECSA群, 图2 ). 2000年刚果民主共和国疫情的分离物[ 6 ]在ECSA组中也形成了一个均匀的分支。 没有ECSA组成员显示出与印度洋分离物有明显更密切的关系。 亚洲分离物与印度洋分离物的亲缘关系更远,构成了ECSA群的姐妹群,而西非分离物的差异更大。 包含其他α病毒,包括最近亲缘的ONN,将基孔肯亚分离物的根放在通向西非谱系群的分支上(未公布的数据)。
图2。 基于部分E1核苷酸序列的基孔肯雅分离物的系统发育关系。
印度洋疫情的分离物(留尼汪岛、塞舌尔岛、马约特岛、毛里求斯和马达加斯加)代表了东非、中非和南非(ECSA)大家族中的一个独特分支。 引导重采样值显示在主要节点上。 为了方便起见,缩短了通向西非谱系群的分支(长度约为15%)。 最大似然分析导致了非常相似的系统发育。
印度洋疫情分离株序列与S27序列的比较显示,05.115分离株中有316个(2.7%)核苷酸替换( 表S5 ). 亚洲分支Nagpur株与05.115株的平均核苷酸差异为5.1%,而西非分支塞内加尔株37997株的差异为15%( 表S5 ). 有趣的是,后一种菌株与东非和印度洋暴发菌株的87-nt部分(9958–10045,位于结构蛋白6K和E1之间的连接处)完全保持不变。 这一部分的序列一致性可能反映了过去西非和东/中非菌株之间的基因重组事件。 不同的是,我们没有找到统计支持( 第页 > 7 × 10 −2 )由于S27和Réunion分离株之间的分裂,尽管一些基因组区域的核苷酸多态性密度不同。
印度洋暴发菌株的基因型变异与微进化情景 2009年5月(nsP3-S358P)和06.27(nsP1-T301I、nsP2-Y642N和nsP3-460del)分离物中观察到非结构蛋白的特定aa变化。 在结构蛋白中,在分离株06.21、06.27和06.49中观察到E1-A226V的变化,在塞舌尔分离株05.209中观察到E2-Q146R的变化。 除了这些非同义的变化外,在2009年5月、6月27日和6月49日还观察到八个沉默的核苷酸替换( 表3 ).
表3。
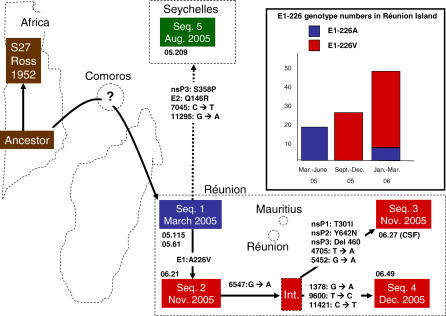
暴发期间可能发生的序列进化史( 图3 )是从6个完整基因组中观察到的14个核苷酸变异中推断出来的( 表3 ). 最初选择分离株05.61进行基因组分析,因为它是在2005年3月疫情爆发时从一名从科摩罗岛返回的留尼汪岛患者身上分离出来的,疫情自2005年1月以来一直在科摩罗发生。 值得注意的是,分离物05.61和05.115(这是所分析的第二个最早的分离物)、非洲分离物S27和以前来自非洲和亚洲的无关基孔肯亚分离物在所有14个多态性位点上都是相同的。 因此,分离株05.61和05.115的一致序列(一致序列1)可能代表了留尼汪暴发的祖先基因型。 14个多态性的分布表明,这位创始人产生了三个可能分四步进化的一致序列。 首先,基因组位置10670处的替换(导致E1 A226V的改变)产生了共识序列2,以2005年11月下旬的分离物06.21为代表。 第二,6547位的G-to-a同义替换(nsP4)导致了一个中间序列,它本身产生了两个晚期序列:共有序列3(分离物06.27),之后有四个额外的替换和一个密码子缺失( 表3 )和一致序列4(06.49),在三个不同的同义替换后出现( 表3 ). 第五个共有序列由塞舌尔分离物(2009年5月)单独代表,与共有序列1相比,共有四个替换(其中两个导致nsP3-S358P和E2-Q146R中aa的变化)( 图3 ).
图3。 印度洋疫情中CHIKV隔离株的拟定进化情景。
该方案基于以RNA提取物为模板获得的RT-PCR产物的直接测序确定的六个基因组序列; 序列(Seq)因此对应于共存基因组(准物种)可能混合的一致序列。
插图:留尼汪岛不同时间间隔的E1-226A和E1-226V病例数,基于部分E1序列。 E1-226V在一致序列2、3和4中被观察到,因此大多数E1-226V分离株基于部分E1序列的基因型可能与这些基因型有关。 然而,不能排除E1-226V在其他基因型中的独立出现。 岛屿和非洲边界的位置、大小和相对位置具有指示性。 共识序列1是从2005年3月从科摩罗回国的一名留尼汪岛患者和一名留尼汪岛病人那里获得的。 序列2-4在留尼汪岛采集; 序列5在塞舌尔采样。 应变代码在相应的序列下给出。 科摩罗群岛的问号表明层序1可能起源于科摩罗。 序列1和序列5之间的虚线链接表明传输路径是假设的。
脑脊液; Int.,推导的中间序列,未取样。
由于留尼汪岛分离株在疫情开始时携带E1-226A,在疫情后期携带E1-226病毒,我们比较了留尼汪岛89名患者共92个序列(87份血清、4份脑脊液和1份羊水)中的残留226。 值得注意的是,E1-226的性质在冬季前后完全不同。 2005年3月16日至6月7日采集的19个患者序列(包括来自科摩罗旅行者的序列)携带E1-226A。 2005年9月7日至12月底,27个序列显示E1-226V。 在2006年的46个Réunion序列中,E1-226V被观察到40次(87%),E1-226 A被观察到6次( 表1 ). 在马达加斯加和塞舌尔序列中,在怀疑第一例临床病例时(即可能在疫情爆发之初),仅观察到E1-226A。 在2005年初爆发疫情的马约特,2006年从患者身上获得的23个序列中只观察到E1-226V。 在2005年爆发疫情的毛里求斯感染患者的序列中,观察到了E1-226A和E1-226V。
讨论 CHIKV目前正在引发过去40年报告的最大基孔肯雅热疫情之一[ 4 – 6 , 29 ]. 尽管基孔肯雅在世界这一地区的附近地区并不罕见,但疫情的严重程度让民众、政策制定者和公共卫生专家感到惊讶。 基于部分糖蛋白E1序列的系统发育分析表明,印度洋疫情是由留尼汪岛、塞舌尔岛、马约特岛、马达加斯加岛和毛里求斯群岛上的同一菌株引起的,并表明疫情菌株与东非、中非和南非分离物有关。 尽管据我们所知,东非最近没有疫情报告,但这种情况与东非和科摩罗之间的人口交流是一致的,据信疫情是从那里开始的。 流行性毒株是否是由一种地方性毒株进化而来的,如之前描述的东部马脑炎病毒[ 30 ],无法排除。 对非洲最近爆发的疫情和可能的当地水库中的其他分离物进行测序,应能更准确地确定印度洋疫情的起源。
据我们所知,这项研究是第一次在基因组尺度上对CHIKV核苷酸变异进行中断内分析的调查。 多个几乎完整的基因组序列的可用性使我们能够推断出疫情仍在发生时可能发生的连续分子进化变化的可能历史。 这种进化场景最有可能基于获得的六个一致序列,尽管需要额外的分离物和准物种异质性的测定,以获得疫情期间病毒进化的更精确图片。
虽然E1-226A是在留尼汪暴发第一阶段(2005年3月至6月)观察到的唯一基因型,但我们的数据显示,E1-226V基因型的出现和优势,这是从2005年9月初观察到的,其频率显著上升。 E1-226V的出现至少比2005年12月中旬的爆发性疫情高峰期提前了3个月,因此,这种aa变化与传播率之间的联系值得进一步调查。 有趣的是,在SFV的226残基处观察到突变,以释放该病毒的胆固醇依赖性[ 27 , 28 ]. 因此,这种突变可能为蚊子体内的病毒提供了一种选择性优势,蚊子是胆固醇营养不良者。 事实上,在SFV E1晶体结构中,位置226位于ij环中,与融合肽接触,位于预计与靶膜相互作用的蛋白质区域。 另一方面,这种变化可能是选择性中性的,而其他进化因素,如遗传漂变或创始人效应,可能只是偶然有利于E1-226V。 在Sindbis病毒中,仅226位的改变不足以释放胆固醇依赖性[ 31 ]. 因此,我们的数据指出了有趣的实验,比较了E1中226位不同菌株的胆固醇依赖性。
迄今为止,只有在蚊子或哺乳动物细胞上多次传代的CHIKV实验室菌株已经完全测序[ 9 ]. 我们首次提供了六个临床分离株的几乎完整的核苷酸序列,这些临床分离株仅在体外传代一次或两次(参见 方法 ). 限制传代数量至关重要,因为感染病毒的群体可能对应于准种[ 32 – 34 ]也就是说,基因型的混合病毒种群在突变和自然选择之间的平衡中共存。 重复的体外传代可能会对该群体起到过滤作用。 例如,在印度洋分离物中,S27中存在Arg密码子而不是蛋白石终止密码子,这可能是由于S27的大量体外传代所致,因为在ONN病毒中实验观察到蛋白石向Arg的进化[ 24 ]. 虽然病毒准种在体内保持蛋白石密码子可能是有利的,但如密切相关的SFV所观察到的,Arg密码子在体外可能具有选择性优势[ 35 ]. 在本研究中,仔细检查色谱图痕迹,发现三个密码子在正向和反向痕迹上都有双峰( 图S3 ). 在这三种情况下,替代碱基对应于非同义密码子,从而可能改变病毒的适应度。 人们很容易推测,体内准物种的多样性可能有助于进入不同的身体部位,例如中枢神经系统。 例如,选择CSF分离物06.27中观察到变化的基因型子集可能与CSF侵袭有关[ 34 ]. 这些观察结果强调,实验室“参考”菌株的基因组序列可能无法准确反映自然情况,因为体内准物种的基因型复杂性会受到体外选择的侵蚀。 由于此处测序的印度洋分离株仅经过几代的体外选择,因此它们可能比之前测序的基孔肯亚菌株更接近体内基因型。
暴发菌株之间检测到的aa差异可能与病毒的生物学或致病特性有关。 虽然我们的病毒培养结果是初步的,但它们清楚地显示了从新生儿脑病病例中分离出的脑脊液独特分离物(06.27)与从与该疾病或脑病的典型形式相关的血清中分离的其他三个分离物之间的表型差异。 在06.27培养基中观察到的较大病灶可能反映出病毒的较高复制率,并与在nsP1、nsP2和nsP3中确定的特定aa变化有关。 nsP1中的单个aa变化,包括Thr/Ile变化(Sindbis病毒的538残基)[ 36 , 37 ]nsP3中的18-nt缺失先前已被证明影响其他α病毒的神经毒力[ 36 – 38 ]. 然而,在缺乏nsP1、nsP2和nsP3结构数据的情况下,很难预测在分离物06.27中观察到的特异性aa变化是否会产生结构或功能影响。 我们还注意到,从三例新生儿脑病病例和一例成人脑膜炎病例的血清或分离物中测定的所有病毒序列均为E1-226V。 然而,由于这种基因型也存在于该病的典型类型中,因此不能得出E1-226V与神经病变的潜在联系的结论。 在神经系统疾病的发生过程中也必须考虑宿主因素。 例如,年龄或高血压可能会促进血脑交叉。
将印度洋爆发基因组的分子特征与所有其他报道的阿尔法病毒序列进行比较时,发现了这些基因组的分子特征。 然而,由于之前的α病毒序列数量较少,可能存在采样偏差,因此必须谨慎考虑这些比较。 然而,这些特征代表了未来功能研究以及流行病学随访的有趣目标。 一个特别有趣的特征是E1-226V残留物(见上文)。 另一个有趣的分子标记是E1-284天冬氨酸。 虽然所用支架的伪原子模型分辨率适中(晶体结构的分辨率有限,接近3º-并且将该结构拟合到9º分辨率的低温电子显微镜重建中的模型结果), 似乎Asp 284的副链与病毒体内相邻E1多肽的主链相互作用。 事实上,它的位置与接触E1原聚体中的主链酰胺的氢键相兼容。 因为填料很紧(参见 图1 B) ,可能较长的谷氨酸侧链(具有额外的CH 2 与Asp或Asn相比,组可能会在接触部位产生轻微畸变,这种效应是由病毒粒子的二十面体T=4对称性传播的。 因此,由于Asp 284位置的这种变化而产生的协同效应可能在受感染细胞中新粒子组装效率较低,或在新细胞入侵期间更有效的粒子拆卸过程中,或两者的结合中发挥作用。 这些信息可以指导使用反向遗传学进行的新的定点突变研究,以测试天冬氨酸/谷氨酸替代物对病毒循环的影响。
此次疫情的规模和高度政治性突出表明,与相关的模式α病毒如Sindbis、Semliki Forest和Ross River相比,CHIKV的生物学知识严重缺乏。 这种情况反映了一个事实,即基孔肯雅病毒感染尽管自发现以来感染了数百万人,但却被忽视了。 然而,基孔肯雅病显然是致残和持续性关节痛的原因,尽管这些症状是由于病毒持续存在还是由于不适当的免疫反应导致的,目前还没有定论[ 39 , 40 ]. 此外,在印度洋CHIKV疫情期间,一小部分患者(约244000名感染者中的123名)出现了严重的临床症状,如神经症状或肝炎。 虽然对几种α病毒(如东部马脑炎病毒和委内瑞拉马脑炎)建立了神经毒力和神经侵袭性,但此前仅从具有脑炎和脑膜炎临床症状的儿童中分离出两株CHIKV病毒[ 41 , 42 ]. CHIKV印度洋毒株是否具有较高的神经毒力或神经侵袭性,当然值得调查。
在缺乏有效疫苗或抗病毒治疗的情况下,媒介控制目前是限制基孔肯雅病毒传播的唯一途径。 然而,蚊子媒介的广泛地理分布 白纹伊蚊 和 埃及伊蚊 [ 43 ]可能允许CHIKV扩展到新的地区,如欧洲或美洲大陆。 此处报告的当前流行性疾病临床分离株的分子数据应有助于弥合关于这种人类病原体的知识差距,并将有助于在中期提供更具体、更有力的工具来对抗它。
支持信息
替代语言摘要S1。 IS将摘要翻译成法语。 (28 KB文档)
图S1。 重复在3′NTR区域发现的序列元素。 (A) CHIKV基因组3′NTR区重复序列元件的比对。 所有序列都形成保守和稳定的干环结构,其中20位附近保守度较低的核苷酸构成环。 在所有基孔肯雅基因组中都发现了三个重复序列元件。 第一个(RSE1)插入S27基因组的内部多A序列之前[ 9 ]而其他两个则位于该图案的下游。 (B) 分离物05–115的RSE1的预测二级结构。
(89 KB PPT)
图S2。 蚊虫细胞CHIKV的焦点大小表型。 蚊子AP61细胞在24孔板(10 5 细胞/孔)感染5–10 FFU/孔或50–100 FFU/孔低通量CHIKV 05.115、06.21、06.27和06.49。 将感染细胞覆盖在含有2%FBS的Leibovitz L-15生长培养基中的羧甲基纤维素上2 d,以便在28°C下形成病灶。 感染细胞用3%多聚甲醛固定于PBS中,用Triton X-100渗透于PBS,CHIK病毒复制灶用抗CHIKV HMAF(稀释度1:2000)和过氧化物酶结合山羊抗鼠Ig(稀释度1:100)进行免疫染色。 直方图描述了由平方像素(相对值)确定的病毒病灶的总面积。
(2.5 MB PPT)
图S3。 三个核苷酸位置的色谱图痕迹显示在两条链上观察到混合峰。 这种峰值可以用准种的存在来解释,即几种不同基因型在体内共存。 第978位(nsP1–301)在三个菌株(05.115、06.21和06.49)中显示了C/T峰(Thr/Ile替换),这三个菌株都是从第2代RNA提取物中测序的。 有趣的是,该位点对应于Réunion分离物06.27(CSF样品,第1代)中的T替代,而不是分离物05.61和其他CHIKV序列中的C。 位置1016在菌株06.49中显示出混合a/G峰,对应于残留nsP1-313的Met或Val。 最后,位置1070在菌株05.115和06.21中显示出A/G峰值,这导致在残基nsP1-331处出现Thr或Ala。
(80 KB PPT)
表S1。 用于RT-PCR和测序的引物。 (20 KB XLS)
表S2。 在S27菌株和印度洋爆发菌株之间观察到的非结构蛋白氨基酸变化。 (21 KB XLS)
表S3。 在S27、Ross菌株和印度洋爆发中观察到的结构基因中的氨基酸变化。 (19 KB XLS)
表S4。 序列用于部分E1序列的系统发育分析。 (14 KB XLS)
表S5。 基于氨基酸和核苷酸(括号中)的选定阿尔法病毒结构(SP)和非结构(NSP)蛋白质的序列相似性百分比。 (17 KB XLS)
致谢 我们感谢南Réunion集团(法国留尼汪圣皮埃尔)的A.Fourmaintraux博士、B.Bouhmani博士、G.Barau博士、Y.Touret博士和P.Tournebize博士,以及法国留尼旺地区观察站的哨兵医生,他们为患者提供了临床信息; 以及C.Gouyette Plate-forme Synthèse d'Oligonucléotides LongsáHaut débit,巴斯德基因组Ile-de-France)和C.Bouchier(Plate-fforme Génomique,巴斯德基因Ile-do-France),帮助进行测序。
作者贡献。 AM、JMR、FP和LB发送生物样本进行病毒分离和测序。 SM、SM和NC分离的病毒株,从生物样品和病毒分离物中进行RT-PCR和病毒RNA提取,LF设计并合成引物。 二、 RL和LD进行RT-PCR和序列反应。 二、 LF、GG和SB组装基因组序列。 IS、II、LF、MCV、SD、FAR和SB分析序列数据。 MPF、ACB和PD促进了CHIKV库存的生产,并进行了免疫荧光分析和病毒RNA提取。 NP、MPF和PD进行焦点免疫分析。 IS、PD、FK、FAR、HZ和SB撰写了手稿。
缩写
aa公司 氨基酸
CHIKV公司 基孔肯亚病毒
CSF公司 脑脊液
联邦调查局 胎牛血清
英国皇家空军 高免疫性腹水
ONN(接通) O'nyong-nyong病毒
SFV(SFV) 塞姆利基森林病毒
脚注
引文:Schuffenecker I、Iteman I、Michault A、Murri S、Frangeul L等(2006)引起印度洋疫情的基孔肯雅病毒基因组微进化。 《公共科学图书馆·医学》3(7):e263。 内政部:10.1371/journal.pmed.0030263
基金: 获得了巴斯德研究所、国家科学研究中心(CNRS)、国家基因组研究所(RNG)和维耶尔·桑泰尔研究所的财政支持。 资助者在研究设计、数据收集和分析、出版决定或手稿准备方面没有任何作用。
工具书类
施特劳斯EG、施特劳斯·JH。 阿尔法病毒基因组的结构和复制。 收录人:施莱辛格S,施莱辛格尔MJ,编辑。 Togaviridae和Flaviviridae。 纽约:Plenum出版社; 1986年,第35-90页。 [ 谷歌学者 ]
Porterfield JH公司。 抗原特征和分类 多哥病毒科 收录人:施莱辛格R,编辑。 多哥病毒。 纽约:学术出版社; 1980年,第13-46页。 [ 谷歌学者 ]
Ross RW,《纽瓦拉疫情》。 三、 病毒:分离、致病特性及其与疫情的关系。 J Hyg.杂志。 1956; 54:177–191. doi:10.1017/s002217240004442。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Jupp PG、McIntosh BM、基孔肯雅病。 收录人:Monath TP,编辑。 虫媒病毒:流行病学和生态学。 博卡拉顿(佛罗里达):CRC出版社; 1988年,第137-157页。 [ 谷歌学者 ]
Johnston RE,Peters CJ。 阿尔法病毒主要与发热和多关节炎有关。 In:Fields BN,Knipe DM,Howley PM,编辑。 菲尔德病毒学。 费城:Lippincott-Raven出版社; 1996年,第843–898页。 [ 谷歌学者 ]
Pastorino B、Muyembe-Tamfum JJ、Bessaud M、Tock F、Tolou H等,《民主刚果共和国基孔肯雅病毒的流行性复苏:一种新的中非毒株的鉴定》。 医学病毒杂志。 2004; 74:277–282. doi:10.1002/jmv.20168。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Laras K、Sukri NC、Larasati RP、Bangs MJ、Kosim R等。追踪印尼流行基孔肯雅病毒的重新出现。 Trans R Soc Trop Med Hyg.公司。 2005; 99:128-141。 doi:10.1016/j.trstmh.2004.03.013。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Paquet C、Quatresous I、Solet JL、Sissoko D、Renault P等。2005年至2006年1月初留尼汪岛基孔肯亚疫情暴发:流行病学和监测。 欧洲监管。 2006; 11点2分。 doi:10.2807/esw.11.05.2891-en。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Khan AH、Morita K、Parquet Md Mdel C、Hasebe F、Mathenge EG等。基孔肯雅病毒的完整核苷酸序列和内部多腺苷酸化位点的证据。 维罗尔将军。 2002年; 83:3075–3084. doi:10.1099/0022-1317-83-12-3075。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Powers AM、Brault AC、Tesh RB、Weaver SC。基孔肯亚病毒和O'nyong-nyong病毒的重新融合:不同地理谱系和遥远进化关系的证据。 维罗尔将军。 2000; 81:471–479. doi:10.1099/0022-1317-81-2-471。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Navarro-Sanchez E、Altmeyer MR、Amara A、Schwartz O、Fieschi F等。DC-SIGN对于蚊子细胞衍生登革热病毒对人类树突状细胞的生产性感染至关重要。 EMBO代表,2003年; 7:1–6. doi:10.1038/sj.embor.embor866。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Gordon D Abajian C,Green P.Consed:序列整理的图形工具。 基因组研究,1998年; 8:195–202. doi:10.1101/gr.8.3.195。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Rozas J,Sanchez-DelBarrio JC,Messeguer X,Rozas R.DnaSP,DNA多态性的结合分析和其他方法。 生物信息学。 2003; 19:2496–2497. doi:10.1093/bioinformatics/btg359。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
夏X,谢Z.DAMBE:分子生物学和进化数据分析软件包。 J赫雷德。 2001; 92:371–373. doi:10.1093/jhered/92.4371。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Thompson JD、Higgins DG、Gibson TJ。聚类W:通过序列加权、位置特定的间隙惩罚和权重矩阵选择提高渐进式多序列比对的敏感性。 《核酸研究》1994; 22:4673–4680. doi:10.1093/nar/22.22.4673。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Felsenstein J.PHYLIP-系统发育推断包(3.2版)分支系统学。 1989; 5:164–166. [ 谷歌学者 ]
Hofacker IL。维也纳RNA二级结构服务器。 核酸研究2003; 31:3429–3431. doi:10.1093/nar/gkg599。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Kumar S、Tamura K、Nei M.MEGA3:分子进化遗传学分析和序列比对的集成软件。 简要生物信息。 2004; 5:150–163. doi:10.1093/bib/5.2.150。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Martin DP,Williamson C,Posada D.RDP2:从序列比对中进行重组检测和分析。 生物信息学。 2005; 21:260–262. doi:10.1093/bioinformatics/bth490。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Roussel A,Lescar J,Vaney MC,Wengler G,Wengler G等。森利基森林病毒包膜蛋白E1的病毒表面结构和相互作用。 结构。 2006; 14:75–86. doi:10.1016/j.str.2005.09.014。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Carson M.高分子带状模型。 J摩尔图。 1987; 5:103–106. [ 谷歌学者 ]
Strauss JH,Strauss EG.α病毒:基因表达、复制和进化。 《微生物学评论》1994; 58:491–562. doi:10.1128/mr.58.3.491-562.1994。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Lavergne A、Thoisy BD、Lacoste V、Pascalis H、Pouliquen JF等。马亚罗病毒:与其他α病毒的完整核苷酸序列和系统发育关系。 2005年病毒研究doi:10.1016/j.virusres.2005.11.006。 新闻界。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Lanciotti RS、Ludwig ML、Rwaguma EB、Lutwama JJ、Kram TM等。在乌干达35年没有奥尼永热疫情的出现:病毒的遗传特征。 病毒学。 1998; 252:258–268. doi:10.1006/viro.1998.9437。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
施特劳斯EG、莱文森R、赖斯CM、达尔林普J、施特劳斯·JH。 Ross River和O'Nyong-Nyong病毒的非结构蛋白nsP3和nsP4:序列和与其他α病毒的比较。 病毒学。 1988; 164:265–274. doi:10.1016/0042-6822(88)90644-7。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
格里芬DE.阿尔法病毒。 In:Knipe DM,Howley PM,编辑。 菲尔德病毒学。 费城:Lippincott Williams&Wilkins; 2001年,第917-962页。 [ 谷歌学者 ]
Vashithha M、Phalen T、Marquardt MT、Ryu JS、Ng AC等。单点突变控制Semliki Forest病毒进入和退出的胆固醇依赖性。 细胞生物学杂志。 1998; 140:91–99. doi:10.1083/jcb.140.1.91。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Ahn A,Schoepp RJ,Sternberg D,Kielian M.一种不依赖胆固醇的Semliki森林病毒突变株在蚊子中的生长和稳定性。 病毒学。 1999; 262:452–456. doi:10.1006/viro.1999.9932。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Williams MC、Woodall JP、Corbet PS、Gillett JD。 奥尼永-尼永热:东非的一种流行性病毒病。 8.疟蚊病毒分离。 Trans R Soc Trop Med Hyg.公司。 1965; 59:300–306。 doi:10.1016/0035-9203(65)90012-x。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Weaver SC,Barrett AD。虫媒病毒病的传播周期、宿主范围、进化和出现。 《自然微生物评论》。 2004; 2:789–801。 doi:10.1038/nrmicro1006。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Lu YE,Casse T,Kielian M。新冠病毒进入和离开的胆固醇需求以及与胆固醇依赖有关的刺突蛋白区域的特征。 《维罗尔杂志》。 1999; 73:4272–4278. doi:10.1128/jvi.73.5.4272-4278.1999。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Holland J、Spindler K、Horodyski F、Grabau E、Nichol S等。RNA基因组的快速进化。 科学。 1982; 215:1577–1585. doi:10.1126/science.7041255。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
多明戈E,Holland JJ。 RNA病毒突变与生存适应性。 微生物年鉴。 1997; 51:151–178. doi:10.1146/annurev.micro.51.1.151。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Vignuzzi M、Stone JK、Arnold JJ、Cameron CE、Andino R.准物种多样性通过病毒群中的合作相互作用确定发病机制。 自然。 2006; 439:344–348. doi:10.1038/nature04388。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Kim KH、Rumenapf T、Strauss EG和Strauss JH。 Semliki森林病毒RNA复制的调控:无脊椎动物宿主中α病毒发病机制的控制模型。 病毒学。 2004; 323:153–163. doi:10.1016/j.virol.2004.03.009。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Heise C,Kirn DH。 复制选择性腺病毒作为溶瘤剂。 临床投资杂志。 2000; 105:847–851. doi:10.1172/JCI9762。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Heise MT、White LJ、Simpson DA、Leonard C、Bernard KA等。Sindbis-group病毒S.A.AR86的nsP1中的减弱突变加快了非结构蛋白处理并上调了病毒26S RNA的合成。 《维罗尔杂志》。 2003; 77:1149–1156. doi:10.1128/JVI.77.2.1149-1156.2003。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Suthar MS、Shabman R、Madric K、Lambeth C、Heise MT。Sindbis病毒株AR86成年小鼠神经毒力决定簇的鉴定。 《维罗尔杂志》。 2005; 79:4219–4228. doi:10.1128/JVI.79.7.2219-4228.2005。 [ 内政部 ] [ PMC免费文章 ] [ 公共医学 ] [ 谷歌学者 ]
Condon RJ,Rouse IL。澳大利亚西南部罗斯河病毒感染的急性症状和后遗症:一项随访研究。 临床诊断病毒。 1995; 3:273–284. doi:10.1016/s0928-0197(94)00043-3。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Selden SM,Cameron AS。南澳大利亚州罗斯河病毒病的流行病学变化。 澳大利亚医学杂志。 1996; 165:313–317. doi:10.5694/j.1326-5377.1996.tb124989.x。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Mazaud R、Salaün JJ、Montabone H、Goube P、Bazilio R。登革热和基孔肯雅病的神经系统和感觉系统问题。 公牛Soc致病性出血热。 1971; 64:22–30. [ 公共医学 ] [ 谷歌学者 ]
Nimmannitya S、Halstead SB、Cohen SN、Margiotta MR。1962年至1964年,泰国男性登革热和基孔肯雅病毒感染。 一、出血热住院患者的观察。 Am J Trop医学杂志。 1969; 18:954–971. doi:10.4269/ajtmh.1969.18.954。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Gratz NG。对 白纹伊蚊 .医学兽医昆虫学。 2004; 18:215–227. doi:10.1111/j.0269-283X.2004.00513.x。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
Lescar J,Roussel A,Wien MW,Navaza J,Fuller SD,et al.Semliki Forest病毒的融合糖蛋白外壳:一种二十面体组装体,在内胚体pH细胞中启动融合激活。 2001; 105:137–148. doi:10.1016/s0092-8674(01)00303-8。 [ 内政部 ] [ 公共医学 ] [ 谷歌学者 ]
关联数据 本节收集本文中包含的任何数据引用、数据可用性声明或补充材料。
补充资料
替代语言摘要S1。 IS将摘要翻译成法语。 (28 KB文档)
图S1。 重复在3′NTR区域发现的序列元素。 (A) CHIKV基因组3′NTR区重复序列元件的比对。 所有序列都形成保守和稳定的干环结构,其中20位附近保守度较低的核苷酸构成环。 在所有基孔肯雅基因组中都发现了三个重复序列元件。 第一个(RSE1)插入S27基因组的内部poly-A序列之前[ 9 ]而其他两个则位于该图案的下游。 (B) 分离物05–115的RSE1的预测二级结构。
(89 KB PPT)
图S2。 蚊虫细胞CHIKV的焦点大小表型。 蚊子AP61细胞在24孔板(10 5 细胞/孔)感染5–10 FFU/孔或50–100 FFU/孔低通量CHIKV 05.115、06.21、06.27和06.49。 将感染细胞覆盖在含有2%FBS的Leibovitz L-15生长培养基中的羧甲基纤维素上2 d,以便在28°C下形成病灶。 感染细胞用3%多聚甲醛固定于PBS中,用Triton X-100渗透于PBS,CHIK病毒复制灶用抗CHIKV HMAF(稀释度1:2000)和过氧化物酶结合山羊抗鼠Ig(稀释度1:100)进行免疫染色。 直方图描述了由平方像素(相对值)确定的病毒病灶的总面积。
(2.5 MB PPT)
图S3。 三个核苷酸位置的色谱图痕迹显示在两条链上观察到混合峰。 这种峰值可以用准物种的存在来解释,即体内几种不同基因型的共存。 第978位(nsP1–301)在三个菌株(05.115、06.21和06.49)中显示了C/T峰(Thr/Ile替换),这三个菌株都是从第2代RNA提取物中测序的。 有趣的是,该位点对应于Réunion分离物06.27(CSF样品,第1代)中的T取代,而不是分离物05.61和其他CHIKV序列中的C。 位置1016在菌株06.49中显示出混合a/G峰,对应于残留nsP1-313的Met或Val。 最后,位置1070在菌株05.115和06.21中显示出A/G峰值,这导致在残基nsP1-331处出现Thr或Ala。
(80 KB PPT)
表S1。 用于RT-PCR和测序的引物。 (20 KB XLS)
表S2。 在S27菌株和印度洋爆发菌株之间观察到的非结构蛋白氨基酸变化。 (21 KB XLS)
表S3。 在S27、Ross菌株和印度洋爆发中观察到的结构基因中的氨基酸变化。 (19 KB XLS)
表S4。 序列用于部分E1序列的系统发育分析。 (14 KB XLS)
表S5。 基于氨基酸和核苷酸(括号中)的选定阿尔法病毒结构(SP)和非结构(NSP)蛋白质的序列相似性百分比。 (17 KB XLS)