PubMed摘要:
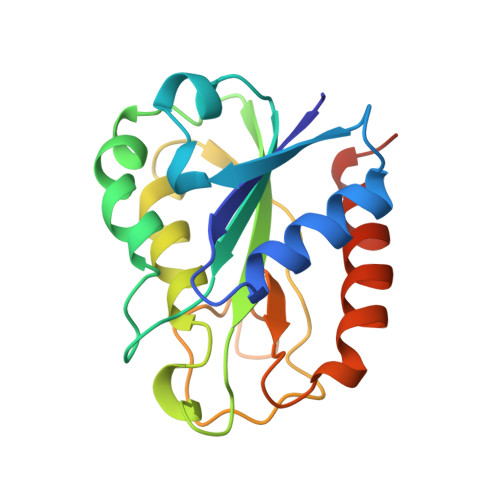
在大肠杆菌中,黄曲霉毒素是丙酮酸甲酸-赖氨酸酶、厌氧核糖核苷酸还原酶和B12依赖性蛋氨酸合成酶的还原激活的生理电子供体。作为黄曲霉毒素与蛋氨酸合成酶相互作用研究的基础,测定了大肠杆菌氧化重组黄曲霉素的正交型和三角型晶体结构。正交形(空间群P2(1)2(1)1(1),a=126.4,b=41.10,c=69.15 a,每个不对称单元有两个分子)最初通过分子替换以3.0 a的分辨率进行求解,使用来自Synerchoccus PCC 7942(Anacystis nidulans)黄曲霉毒素结构的坐标。在140 K下收集分辨率达到1.8-A的数据,并将结构细化为Rwork 0.196和Rfree 0.250(对于I>0的反射)。最终的模型每个不对称单元包含3224个非氢原子,包括62个黄素单核苷酸(FMN)原子、354个水分子、四个钙离子、四个钠离子、两个氯离子和两个双三缓冲分子。使用正交结构的坐标,通过分子替换求解三角形形式的蛋白质结构(空间群P312,a=78.83,c=52.07A),并使用10.0到2.6A的所有数据进行细化(R=0.191;Rfree=0.249)。序列Tyr 58-Tyr 59位于FMN附近的一个弯道上,迄今为止仅在大肠杆菌和流感嗜血杆菌的黄曲霉毒素中发现,它可能在黄曲霉素与其激活反应伙伴的相互作用中起重要作用。该弯曲中的酪氨酸残基受分子间接触的影响,在两种晶型中采用不同的取向。与来自聚球藻PCC 7942和阿那贝纳PCC 7120的黄曲霉毒素的结构比较表明,其他残基也可能对蛋氨酸合成酶的识别至关重要。