提升阀版本2

是什么爆裂声?
波普尔是一个R包,用于分析有性繁殖和克隆繁殖混合模式的种群。它是围绕以下框架构建的阿德杰内特的gennd和genlight对象,并提供以下实现:
- 一个层次结构中任意多个层次上种群的克隆审查
- 多位点基因型的简便计数和多层次群体的亚群体
- 定义多位点基因型
- 基因型多样性、均匀度、丰富度和稀疏度指数的计算
- 基于bootstrap支持的遗传距离树形图绘制
- 遗传距离最小生成网络的绘制
- 关联指数的计算(
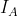 )或(
)或(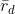 )
)
- 在安装了R(≥2.15.1)的任何服务器上进行批处理
- 微卫星(SSR)标记的Bruvo距离计算(用C表示速度)
- 从导入数据并导出到通用航空公司
2.0版中的新增功能:
- 基因组SNP数据的处理
- 自定义多点基因型定义
- 利用遗传距离瓦解多点谱系
- 计算网状最小跨度网络
- 跨snp计算滑动窗口中的关联索引
- MLG多样性统计的自举
- 最小跨越网络的交互式探索
- 还有更多!
有关详细信息,请参阅NEWS文件或在R控制台中键入:
引用
如果您使用爆裂声总之,请指定版本并引用:
Kamvar ZN,Tabima JF,新泽西州Grünwald。(2014)Poppr:克隆、部分克隆和/或有性繁殖种群遗传分析的R包。同行J 2:e281https://doi.org/10.7717/peerj.281
如果您使用爆裂声在演示文稿中,请将其作为爆裂声R包,指定版本,并使用我们的徽标:(巴布亚新几内亚)|(svg).
此外,如果您使用以下任何功能:
- 具有网状结构的最小跨越网络
- 将多位点基因型分解为多位点谱系
mlg.过滤器()
- 自定义多点基因型定义
mlg.自定义()
- 基因组数据与
赢.ia()或采样.ia()
- 用genind、genlight或genpop对象引导任何遗传距离
aboot()
还请引用:
Kamvar ZN、Brooks JC和Grünwald NJ(2015)《分析全基因组群体遗传数据的新型R工具》,重点是克隆性。前面。基因。6:208. 数字对象标识:10.3389/fgene.2015.00208年
您可以通过键入以下内容在R中获取引文信息:
安装
来自CRAN
mac和windows的二进制版本适用于R≥2.15.1在这里.
要安装,请确保R的版本至少为2.15.1(作者建议≥3.0),并在控制台中键入:
如果您想要绝对最新版本的爆裂声,请参阅下面有关安装未发布版本的信息。
稳定版本
偶尔会向{poppr}添加新功能,但它可能需要一些时间才能到达CRAN。如果您知道您想要最新版本的{popper}(它将包含错误修复和未来版本中包含的新功能),那么您可以使用自定义R-Universe存储库,该存储库每小时更新一次:https://zkamvar.r-universe.dev/builds网站
要从R-Universe安装poppr,可以使用以下代码:
universe存储库还包含最新版本的{adegenet}和{hierfstat},它们通常与{poppr}结合使用,在CRAN上已经过时了。
不稳定/开发版本
{poppr}的所有开发版本都将在GitHub上,但需要编译。
要从github安装此软件包,请确保您具备以下条件:
- X代码(OSX)或R工具(Windows)
- {远程}(要安装,请使用:
install.packages(“远程”))
对于Linux用户,确保函数getOption(“解压缩”)收益“解压缩”或“内部”。如果没有,则运行选项(unzip=“内部”).
一旦安装了{remotes}和C编译器,就可以使用安装github()函数从github安装当前版本。
测试中的所有新功能都将在不同的分支上发布。这些功能将处于不同的开发阶段,可能会记录,也可能不会记录。安装时要小心。下面的命令将在名为“devel”的分支上安装特性。请注意,这些分支可能已从主分支过期。注意:如果未安装LaTeX,则应设置build_vignettes=错误.
帮助/文档
R文件
要访问帮助文件的描述性索引,请执行以下操作:爆裂声,在控制台中键入:
渐晕
为popper写了几个小插曲:
| 算法和方程 |
渐晕(“algo”,“poppr”) |
| 数据导入和操作 |
vignette(“poppr_manual”,“poppr”) |
| 多位点基因型分析 |
渐晕(“mlg”,“poppr”) |
用户组
对于任何版本的poppr(稳定版或开发版)有任何疑问/意见/建议的用户应将其意见发送给Poppr谷歌组
书籍/初级读物
2014年春天,Niklaus J.Grünwald博士、Sydney E.Everhart博士和Zhian N.Kamvar在位于https://grunwaldlab.github.io/Polpulation_Genetics_in_R。
贡献
请注意,此项目发布时带有贡献者行为准则。参与此项目即表示您同意遵守其条款。如果您希望将代码贡献给爆裂声,请分叉存储库并使用添加的功能创建拉请求。

